La presencia de arsénico en la naturaleza debido a las erupciones volcánicas ha sido una de las amenazas más importantes para el desarrollo de la vida en la tierra. Hoy en día el arsénico presente en los suelos, puede ser solubilizado en las aguas subterráneas exponiendo a los organismos a uno de los carcinógenos más potentes que se conocen. De hecho la exposición a arsénico es responsable del envenenamiento masivo más importante que ha sufrido la humanidad en toda su historia.
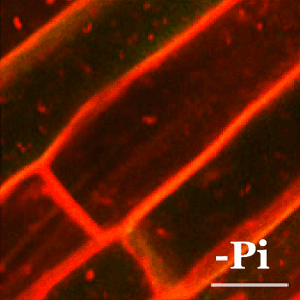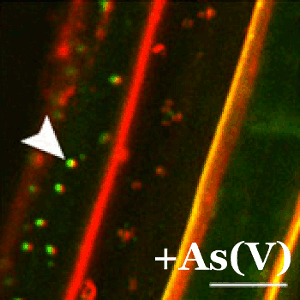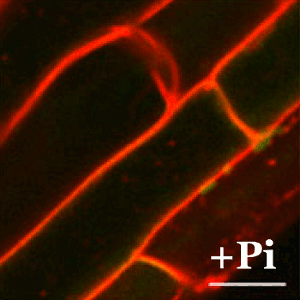 En plantas, la tolerancia al arsénico es esencial para su supervivencia ya que la forma química más abundante en la tierra (el arseniato) guarda una gran similitud con el fosfato y las plantas lo incorporan fácilmente a sus células a través de los transportadores de fosfato. En el CNB, el grupo dirigido por Antonio Leyva estudia las bases moleculares de los mecanismos de percepción de arsénico en plantas con el fin de identificar y desarrollar plantas que eviten la exposición de este carcinógeno a los seres vivos.
En plantas, la tolerancia al arsénico es esencial para su supervivencia ya que la forma química más abundante en la tierra (el arseniato) guarda una gran similitud con el fosfato y las plantas lo incorporan fácilmente a sus células a través de los transportadores de fosfato. En el CNB, el grupo dirigido por Antonio Leyva estudia las bases moleculares de los mecanismos de percepción de arsénico en plantas con el fin de identificar y desarrollar plantas que eviten la exposición de este carcinógeno a los seres vivos.
En este trabajo, merecedor de un comentario especial por parte de los editores de la revista Plant Cell, el grupo de Leyva ha descubierto que cuando las plantas detectan el arseniato impiden de forma inmediata su captación mediante la represión y deslocalización del transportador de fosfato. Este sistema está controlado mediante la acción de una proteína represora conocida como WRKY6.
En colaboración con otros dos grupos del CNB, han podido además descubrir que el arseniato provoca la activación masiva de transposones, unos elementos del ADN móviles capaces de “saltar” de un sitio a otro del genoma en respuesta a estrés y por tanto actuar como agentes mutagénicos. Una activación que también está controlada por el represor WRKY6.
Estos resultados indican que las plantas poseen un mecanismo de percepción del arseniato que controla la activación de transposones y la incorporación del arseniato. Todo ello proporciona un sistema integrado de tolerancia y de estabilidad genómica.
- Castrillo G, Sánchez-Bermejo E, de Lorenzo L, Crevillén P, Fraile-Escanciano A, Tc M, Mouriz A, Catarecha P, Sobrino-Plata J, Olsson S, Leo Del Puerto Y, Mateos I, Rojo E, Hernández LE, Jarillo JA, Piñeiro M, Paz-Ares J, Leyva A. WRKY6 transcription factor restricts arsenate uptake and transposon activation in Arabidopsis. Plant Cell 2013 Aug 6 tpc.113.114009.
Curr Proteomics. 2013; 10(2):83-97
Casado-Vela J, González-González M, Matarraz S, Martínez-Esteso MJ, Vilella M, Sayagues JM, FuentesM, Lacal JC.
 Protein arrays represent a step forward in proteomic technologies, as they enable to address biological and functional questions by large-scale approaches (i.e., up to several thousand proteins may be monitored in a single experiment). Here we review recent achievements of protein arrays and their classification. We also summarize current and future applications of this technology to address the study of the human proteome including protein identification, biomarker discovery, screening of protein-protein/molecule interactions, detection of protein post-translational modifications and serum profiling.
Protein arrays represent a step forward in proteomic technologies, as they enable to address biological and functional questions by large-scale approaches (i.e., up to several thousand proteins may be monitored in a single experiment). Here we review recent achievements of protein arrays and their classification. We also summarize current and future applications of this technology to address the study of the human proteome including protein identification, biomarker discovery, screening of protein-protein/molecule interactions, detection of protein post-translational modifications and serum profiling.
Advantages and limitations of protein arrays compared to other proteomic technologies are also discussed here. The use, advances and recent applications of fluorescent microspheres as a promising alternative to planar arrays are also summarized in this report. Finally, we propose future perspectives of protein arrays from a comprehensive standpoint that includes technological, biological, economical and practical aspects.
Nikel PI, de Lorenzo V.
 Pseudomonas putida KT2440, a microbial cell factory of reference for industrial whole-cell biocatalysis, is unable to support biochemical reactions that occur under anoxic conditions, limiting its utility for a large number of relevant biotransformations. Unlike (facultative) anaerobes, P. putida resorts to NADH oxidation via an oxic respiratory chain and completely lacks a true fermentation metabolism. Therefore, it cannot achieve the correct balances of energy and redox couples (i.e., ATP/ADP and NADH/NAD+) that are required to sustain an O2-free lifestyle.
Pseudomonas putida KT2440, a microbial cell factory of reference for industrial whole-cell biocatalysis, is unable to support biochemical reactions that occur under anoxic conditions, limiting its utility for a large number of relevant biotransformations. Unlike (facultative) anaerobes, P. putida resorts to NADH oxidation via an oxic respiratory chain and completely lacks a true fermentation metabolism. Therefore, it cannot achieve the correct balances of energy and redox couples (i.e., ATP/ADP and NADH/NAD+) that are required to sustain an O2-free lifestyle.
To overcome this state of affairs, the acetate kinase (ackA) gene of the facultative anaerobe Escherichia coli and the pyruvate decarboxylase (pdc) and alcohol dehydrogenase II (adhB) genes of the aerotolerant Zymomonas mobilis were knocked-in to a wild-type P. putida strain. Biochemical and genetic assays showed that conditional expression of the entire enzyme set allowed the engineered bacteria to adopt an anoxic regime that maintained considerable metabolic activity. The resulting strain was exploited as a host for the heterologous expression of a 1,3-dichloroprop-1-ene degradation pathway recruited from Pseudomonas pavonaceae 170, enabling the recombinants to degrade this recalcitrant chlorinated compound anoxically. These results underscore the value of P. putida as a versatile agent for biotransformations able to function at progressively lower redox statuses.
DNA Repair (Amst). 2013 Mar 1;12(3):162-76
Alonso JC, Cardenas PP, Sanchez H, Hejna J, Suzuki Y, Takeyasu K.
 All organisms rely on integrated networks to repair DNA double-strand breaks (DSBs) in order to preserve the integrity of the genetic information, to re-establish replication, and to ensure proper chromosomal segregation. Genetic, cytological, biochemical and structural approaches have been used to analyze how Bacillus subtilis senses DNA damage and responds to DSBs.
All organisms rely on integrated networks to repair DNA double-strand breaks (DSBs) in order to preserve the integrity of the genetic information, to re-establish replication, and to ensure proper chromosomal segregation. Genetic, cytological, biochemical and structural approaches have been used to analyze how Bacillus subtilis senses DNA damage and responds to DSBs.
RecN, which is among the first responders to DNA DSBs, promotes the ordered recruitment of repair proteins to the site of a lesion. Cells have evolved different mechanisms for efficient end processing to create a 3′-tailed duplex DNA, the substrate for RecA binding, in the repair of one- and two-ended DSBs. Strand continuity is re-established via homologous recombination (HR), utilizing an intact homologous DNA molecule as a template. In the absence of transient diploidy or of HR, however, two-ended DSBs can be directly re-ligated via error-prone non-homologous end-joining. Here we review recent findings that shed light on the early stages of DSB repair in Firmicutes.
Castrillo G, Sánchez-Bermejo E, de Lorenzo L, Crevillén P, Fraile-Escanciano A, Tc M, Mouriz A, Catarecha P, Sobrino-Plata J, Olsson S, Leo Del Puerto Y, Mateos I, Rojo E, Hernández LE, Jarillo JA, Piñeiro M, Paz-Ares J, Leyva A.
 Stress constantly challenges plant adaptation to the environment. Of all stress types, arsenic was a major threat during the early evolution of plants. The most prevalent chemical form of arsenic is arsenate, whose similarity to phosphate renders it easily incorporated into cells via the phosphate transporters.
Stress constantly challenges plant adaptation to the environment. Of all stress types, arsenic was a major threat during the early evolution of plants. The most prevalent chemical form of arsenic is arsenate, whose similarity to phosphate renders it easily incorporated into cells via the phosphate transporters.
Here, we found that arsenate stress provokes a notable transposon burst in plants, in coordination with arsenate/phosphate transporter repression, which immediately restricts arsenate uptake. This repression was accompanied by delocalization of the phosphate transporter from the plasma membrane. When arsenate was removed, the system rapidly restored transcriptional expression and membrane localization of the transporter.
We identify WRKY6 as an arsenate-responsive transcription factor that mediates arsenate/phosphate transporter gene expression and restricts arsenate-induced transposon activation. Plants therefore have a dual WRKY-dependent signaling mechanism that modulates arsenate uptake and transposon expression, providing a coordinated strategy for arsenate tolerance and transposon gene silencing.
J Biol Chem. 2013 Jul 19;288(29):20830-6
Rico AI, Krupka M, Vicente M.
 Cell division in Escherichia coli begins by assembling three proteins, FtsZ, FtsA, and ZipA, to form a proto-ring at midcell. These proteins nucleate an assembly of at least 35 components, the divisome. The structuring of FtsZ to form a ring and the processes that effect constriction have been explained by alternative but not mutually exclusive mechanisms.
Cell division in Escherichia coli begins by assembling three proteins, FtsZ, FtsA, and ZipA, to form a proto-ring at midcell. These proteins nucleate an assembly of at least 35 components, the divisome. The structuring of FtsZ to form a ring and the processes that effect constriction have been explained by alternative but not mutually exclusive mechanisms.
We discuss how FtsA and ZipA provide anchoring of the cytoplasmic FtsZ to the membrane and how a temporal sequence of alternative protein interactions may operate in the maturation and stability of the proto-ring. How the force needed for constriction is generated and how the proto-ring proteins relate to peptidoglycan synthesis remain as the main challenges for future research.
Mol Cell Proteomics. 2013 Aug;12(8):2332-40
Walzer M, Qi D, Mayer G, Uszkoreit J, Eisenacher M, Sachsenberg T, Gonzalez-Galarza FF, Fan J, Bessant C, Deutsch EW, Reisinger F, Vizcaíno JA, Medina-Aunon JA, Albar JP, Kohlbacher O, Jones AR.
 The range of heterogeneous approaches available for quantifying protein abundance via mass spectrometry (MS) leads to considerable challenges in modeling, archiving, exchanging, or submitting experimental data sets as supplemental material to journals. To date, there has been no widely accepted format for capturing the evidence trail of how quantitative analysis has been performed by software, for transferring data between software packages, or for submitting to public databases.
The range of heterogeneous approaches available for quantifying protein abundance via mass spectrometry (MS) leads to considerable challenges in modeling, archiving, exchanging, or submitting experimental data sets as supplemental material to journals. To date, there has been no widely accepted format for capturing the evidence trail of how quantitative analysis has been performed by software, for transferring data between software packages, or for submitting to public databases.
In the context of the Proteomics Standards Initiative, we have developed the mzQuantML data standard. The standard can represent quantitative data about regions in two-dimensional retention time versus mass/charge space (called features), peptides, and proteins and protein groups (where there is ambiguity regarding peptide-to-protein inference), and it offers limited support for small molecule (metabolomic) data. The format has structures for representing replicate MS runs, grouping of replicates (for example, as study variables), and capturing the parameters used by software packages to arrive at these values. The format has the capability to reference other standards such as mzML and mzIdentML, and thus the evidence trail for the MS workflow as a whole can now be described. Several software implementations are available, and we encourage other bioinformatics groups to use mzQuantML as an input, internal, or output format for quantitative software and for structuring local repositories. All project resources are available in the public domain from the HUPO Proteomics Standards Initiative.
Fungal Genet Biol. 2013 Jul 18. pii: S1087-1845(13)00126-6
Valencia EY, Chambergo FS.
 Brazil houses over 10% of the total number of known species on Earth, with a great diversity of plants and fungi. The collection, isolation, identification and conservation of filamentous fungi with relevance to agriculture, pharmaceutical, food and biotechnological industries in Biological Resource Centers (CRBs) is very important to the development of a nation's scientific and technological infrastructure. In Brazil, 36 fungal collections are registered in the database of International Collections. Several federal and state programs have encouraged the formation of a researcher's network in order to study natural resources and the nation's biodiversity.
Brazil houses over 10% of the total number of known species on Earth, with a great diversity of plants and fungi. The collection, isolation, identification and conservation of filamentous fungi with relevance to agriculture, pharmaceutical, food and biotechnological industries in Biological Resource Centers (CRBs) is very important to the development of a nation's scientific and technological infrastructure. In Brazil, 36 fungal collections are registered in the database of International Collections. Several federal and state programs have encouraged the formation of a researcher's network in order to study natural resources and the nation's biodiversity.
In this context, Brazilian researchers have been on the frontiers of knowledge, investigating the enzymatic systems from native filamentous fungi with potential for biomass degradation and biotechnological application. In this review, we address recent progress in Brazilian fungal research, focusing on the identification and study of fungi and enzymes with potential for biomass degradation and application in bioenergy.
J Struct Biol. 2013 Feb;181(2):136-48
Vargas J, Otón J, Marabini R, Jonic S, de la Rosa-Trevín JM, Carazo JM, Sorzano CO.
 In this work we present a fast and automated algorithm for estimating the contrast transfer function (CTF) of a transmission electron microscope. The approach is very suitable for High Throughput work because:
In this work we present a fast and automated algorithm for estimating the contrast transfer function (CTF) of a transmission electron microscope. The approach is very suitable for High Throughput work because:
- (a) it does not require any initial defocus estimation,
- (b) it is almost an order of magnitude faster than existing approaches
- (c) it opens the way to well-defined extensions to the estimation of higher order aberrations, at the same time that provides defocus and astigmatism estimations comparable in accuracy to well established methods, such as Xmipp and CTFFIND3 approaches
The new algorithm is based on obtaining the wrapped modulating phase of the power spectra density pattern by the use of a quadrature filter. This phase is further unwrapped in order to obtain the continuous and smooth absolute phase map; then a Zernike polynomial fitting is performed and the defocus and astigmatism parameters are determined. While the method does not require an initial estimation of the defocus parameters or any non-linear optimization procedure, these approaches can be used if further refinement is desired. Results of the CTF estimation method are presented for standard negative stained images, cryo-electron microscopy images in the absence of carbon support, as well as micrographs with only ice. Additionally, we have also tested the proposed method with micrographs acquired from tilted and untilted samples, obtaining good results. The algorithm is freely available as a part of the Xmipp package [http://xmipp.cnb.csic.es].
Protein Expr Purif. 2013 Jul 12. pii: S1046-5928(13)00120-4
Salema V, Fernández LA.
 Nanobodies (Nbs) are single domain antibodies based on the variable domains of heavy chain only antibodies (HCAbs) found in camelids, also referred to as VHHs. Their small size (ca. 12-15 kDa), superior biophysical and antigen binding properties have made Nbs very attractive molecules for multiple biotechnological applications, including human therapy. The most widely used system for the purification of Nbs is their expression in the periplasm of E. coli with a C-terminal hexa-histidine (His6) tag followed by immobilized metal affinity chromatography (IMAC). However, significant variability in the expression levels of different Nbs are routinely observed and a single affinity chromatography step is often not sufficient to obtain Nbs of high purity.
Nanobodies (Nbs) are single domain antibodies based on the variable domains of heavy chain only antibodies (HCAbs) found in camelids, also referred to as VHHs. Their small size (ca. 12-15 kDa), superior biophysical and antigen binding properties have made Nbs very attractive molecules for multiple biotechnological applications, including human therapy. The most widely used system for the purification of Nbs is their expression in the periplasm of E. coli with a C-terminal hexa-histidine (His6) tag followed by immobilized metal affinity chromatography (IMAC). However, significant variability in the expression levels of different Nbs are routinely observed and a single affinity chromatography step is often not sufficient to obtain Nbs of high purity.
Here, we report an alternative method for expression and purification of Nbs from the periplasm of E. coli based on their fusion to maltose binding protein (MBP) in the N-terminus and His6 tag in the C-terminus (MBP-NbHis6). Soluble MBP-NbHis6 fusions were consistently expressed at high levels (⩾12 mg/L of induced culture in shake flasks) in the periplasm of E. coli HM140, a strain deficient in several periplasmic proteases. Highly pure MBP-NbHis6 fusions and free NbHis6 (after site specific proteolysis of the fusions), were recovered by amylose and metal affinity chromatography steps. The monomeric nature of the purified NbHis6 was determined by gel filtration chromatography. Lastly, we demonstrated by ELISA that both monomeric NbHis6 and MBP-NbHis6 fusions retained antigen binding activity and specificity, thus facilitating their direct use in antigen recognition assays.
POLÍTICA DE COOKIES
Una cookie es un archivo de texto que se almacena en el ordenador o dispositivo móvil mediante un servidor Web y tan solo ese servidor será capaz de recuperar o leer el contenido de la cookie y permiten al Sitio Web recordar preferencias de navegación y navegar de manera eficiente. Las cookies hacen la interacción entre el usuario y el sitio Web más rápida y fácil.
Información general
Está página Web utiliza cookies. Las cookies son pequeños archivos de texto generados por las páginas web que usted visita, las cuales contienen los datos de sesión que pueden ser de utilidad posteriormente en la página web. De esta forma esta Web recuerda información sobre su visita, lo que puede facilitar su próxima visita y hacer que el sitio Web le resulte más útil.
¿Cómo funcionan las cookies?
Las cookies sólo pueden almacenar texto, por lo general siempre es anónimo y cifrado. No se almacenarán información personal alguna en una cookie, ni pueden asociarse a persona identificada o identificable.
Los datos permiten que esta Web pueda mantener su información entre las páginas, y también para analizar la forma de interactuar con el sitio Web. Las cookies son seguras ya que sólo pueden almacenar la información que se puso en su lugar por el navegador, lo que es información que el usuario ha introducido en el navegador o la que se incluye en la solicitud de página. No puede ejecutar el código y no se puede utilizar para acceder a su ordenador. Si una página web cifra la información de la cookie, sólo la página web puede leer la información.
¿Qué tipos de cookies utilizamos?
Las cookies que utiliza esta página Web se pueden distinguir según los siguientes criterios:
1. Tipos de cookies según la entidad que las gestiona:
Según quien sea la entidad que gestione el equipo o dominio desde donde se envían las cookies y trate los datos que se obtengan, podemos distinguir:
- Cookies propias: son aquellas que se envían al equipo terminal del usuario desde un equipo o dominio gestionado por el propio editor y desde el que se presta el servicio solicitado por el usuario.
- Cookies de terceros: son aquellas que se envían al equipo terminal del usuario desde un equipo o dominio que no es gestionado por el editor, sino por otra entidad que trata los datos obtenidos través de las cookies.
En el caso de que las cookies sean instaladas desde un equipo o dominio gestionado por el propio editor pero la información que se recoja mediante éstas sea gestionada por un tercero, no pueden ser consideradas como cookies propias.
2. Tipos de cookies según el plazo de tiempo que permanecen activadas:
Según el plazo de tiempo que permanecen activadas en el equipo terminal podemos distinguir:
- Cookies de sesión: son un tipo de cookies diseñadas para recabar y almacenar datos mientras el usuario accede a una página web. Se suelen emplear para almacenar información que solo interesa conservar para la prestación del servicio solicitado por el usuario en una sola ocasión (p.e. una lista de productos adquiridos).
- Cookies persistentes: son un tipo de cookies en el que los datos siguen almacenados en el terminal y pueden ser accedidos y tratados durante un periodo definido por el responsable de la cookie, y que puede ir de unos minutos a varios años.
3. Tipos de cookies según su finalidad:
Según la finalidad para la que se traten los datos obtenidos a través de las cookies, podemos distinguir entre:
- Cookies técnicas: son aquellas que permiten al usuario la navegación a través de una página web, plataforma o aplicación y la utilización de las diferentes opciones o servicios que en ella existan como, por ejemplo, controlar el tráfico y la comunicación de datos, identificar la sesión, acceder a partes de acceso restringido, recordar los elementos que integran un pedido, realizar el proceso de compra de un pedido, realizar la solicitud de inscripción o participación en un evento, utilizar elementos de seguridad durante la navegación, almacenar contenidos para la difusión de vídeos o sonido o compartir contenidos a través de redes sociales.
- Cookies de personalización: son aquellas que permiten al usuario acceder al servicio con algunas características de carácter general predefinidas en función de una serie de criterios en el terminal del usuario como por ejemplo serian el idioma, el tipo de navegador a través del cual accede al servicio, la configuración regional desde donde accede al servicio, etc.
- Cookies de análisis: son aquellas que permiten al responsable de las mismas, el seguimiento y análisis del comportamiento de los usuarios de los sitios web a los que están vinculadas. La información recogida mediante este tipo de cookies se utiliza en la medición de la actividad de los sitios web, aplicación o plataforma y para la elaboración de perfiles de navegación de los usuarios de dichos sitios, aplicaciones y plataformas, con el fin de introducir mejoras en función del análisis de los datos de uso que hacen los usuarios del servicio.
Herramienta de gestión de las cookies
Está página Web utiliza Google Analytics.
Google Analytics es una herramienta gratuita de análisis web de Google que principalmente permite que los propietarios de sitios web conozcan cómo interactúan los usuarios con su sitio web. Asimismo, habilita cookies en el dominio del sitio en el que te encuentras y utiliza un conjunto de cookies denominadas "__utma" y "__utmz" para recopilar información de forma anónima y elaborar informes de tendencias de sitios web sin identificar a usuarios individuales.
Para realizar las estadísticas de uso de esta Web utilizamos las cookies con la finalidad de conocer el nivel de recurrencia de nuestros visitantes y los contenidos que resultan más interesantes. De esta manera podemos concentrar nuestros esfuerzos en mejorar las áreas más visitadas y hacer que el usuario encuentre más fácilmente lo que busca. En esta Web puede utilizarse la información de su visita para realizar evaluaciones y cálculos estadísticos sobre datos anónimos, así como para garantizar la continuidad del servicio o para realizar mejoras en sus sitios Web. Para más detalles, consulte en el siguiente enlace la política de privacidad [http://www.google.com/intl/es/policies/privacy/]
Cómo gestionar las cookies en su equipo: la desactivación y eliminación de las cookies
Todos los navegadores de Internet le permiten limitar el comportamiento de una cookie o desactivar las cookies dentro de la configuración o las opciones del navegador. Los pasos para hacerlo son diferentes para cada navegador, se pueden encontrar instrucciones en el menú de ayuda de su navegador.
Si no acepta el uso de las cookies, ya que es posible gracias a los menús de preferencias o ajustes de su navegador, rechazarlas, este sitio Web seguirá funcionando adecuadamente sin el uso de las mismas.
Puede usted permitir, bloquear o eliminar las cookies instaladas en su equipo mediante la configuración de las opciones del navegador instalado en su ordenador:
- Para más información sobre Internet Explorer pulse aquí.
- Para más información sobre Chrome pulse aquí.
- Para más información sobre Safari pulse aquí.
- Para más información sobre Firefox pulse aquí.
A través de su navegador, usted también puede ver las cookies que están en su ordenador, y borrarlas según crea conveniente. Las cookies son archivos de texto, los puede abrir y leer el contenido. Los datos dentro de ellos casi siempre están cifrados con una clave numérica que corresponde a una sesión en Internet por lo que muchas veces no tienen sentido más allá que la página web que los escribió.
Consentimiento informado
La utilización de la presente página Web por su parte, implica que Vd. presta su consentimiento expreso e inequívoco a la utilización de cookies, en los términos y condiciones previstos en esta Política de Cookies, sin perjuicio de las medidas de desactivación y eliminación de las cookies que Vd. pueda adoptar, y que se mencionan en el apartado anterior.





