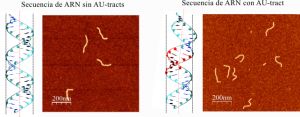
Alberto Marín, investigador del CNB-CSIC y primer autor del trabajo explica: “realizando comparaciones computacionales de una variedad de moléculas de ARN con distintas secuencias hemos observado que aquellas que contenían regiones concretas con bases de adenina y uracilo seguidos (AU-tracts) se curvaban, a diferencia de las moléculas que no incorporaban estas secuencias. Fue un resultado totalmente inesperado”. Para confirmar estos resultados, los investigadores han diseñado moléculas de ARN con secuencias AU-tracts y analizado su disposición utilizando un microscopio de fuerzas atómicas (AFM). “De esta forma, hemos comprobado que las secuencias AU-tracts en las moléculas individuales de ARN de doble hebra modulan la curvatura del ARN”, detalla Fernando Moreno-Herrero, uno de los investigadores que han liderado el trabajo.
Este descubrimiento abre muchas preguntas a explorar en el futuro. Según Mikel Marín, coautor del trabajo “queda por entender qué papel juegan estas estructuras de ARN en el interior de la célula y cómo regulan las interacciones entre ARN y proteínas”. Más allá de su papel en biología, las estructuras de los AU-tracts abren la puerta a diseñar moléculas de ARN con determinadas propiedades estructurales. “Nuestro descubrimiento podría contribuir a impulsar la nanotecnología basada en ARN. Este es un campo relativamente reciente, pero muy prometedor. Tiene por objetivo construir estructuras tridimensionales de ARN en la nanoescala con aplicaciones en nanomedicina, como la administración de fármacos o el diagnóstico mediante biosensores; o en nanotecnología, por ejemplo permitiendo la fabricación de estructuras que podrían servir como andamio en ingeniería de tejidos”.
Más información
Double Stranded RNA bending by AU-tract sequences
A Marín-González, C Aicart-Ramos, M Marin-Baquero, A Martín-González, M Suomalainen, A Kannan, JG Vilhena, UF Greber, F Moreno-Herrero and R Pérez
Nucleic Acids Research, 2020 doi: 10.1093/nar/gkaa1128