Entre los procesos controlados por el sistema Rcs se incluyen el movimiento de la bacteria y la formación de una cápsula protectora. En este trabajo se ha visualizado a nivel atómico como RcsB reconoce y se une su ADN diana, lo que ha permitido identificar su secuencia de reconocimiento y así explicar su especificidad de unión. Esta secuencia (denominada ‘caja’ en el argot) se ha buscado en todo el genoma de Salmonella, encontrándose más de 200 sitios de unión y estando más de la mitad de ellos en regiones con información de codificación de proteínas.
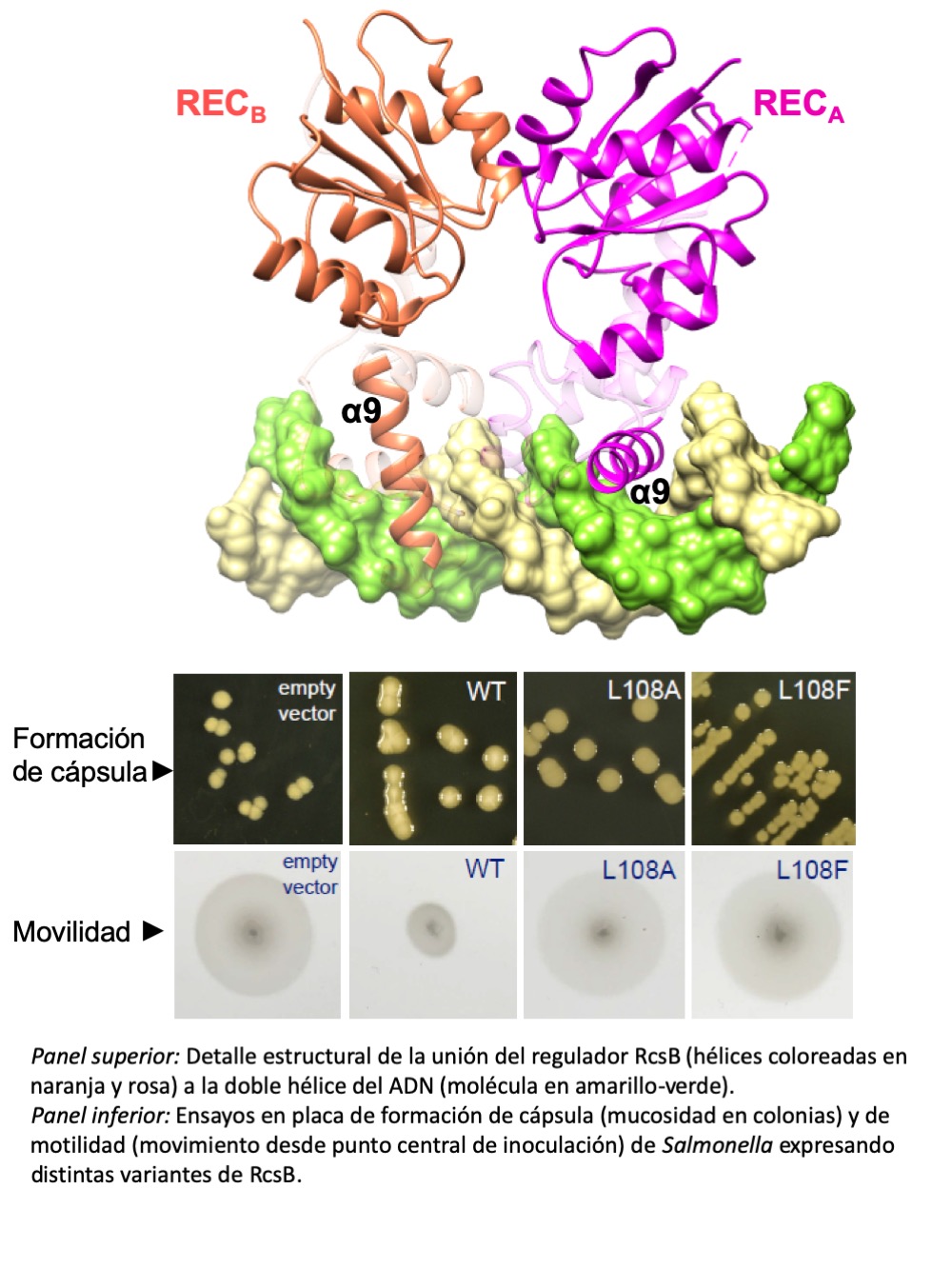
“Mediante este trabajo hemos realizado la mejor caracterización hasta la fecha del sistema Rcs de Salmonella, descubriendo que gestiona más genes de los que pensábamos, hasta un centenar, entre ellos algunos fundamentales para la supervivencia de la bacteria en nuestro organismo”, explica Alberto Marina, investigador del Instituto de Biomedicina de Valencia (IBV-CSIC) y uno de los coautores del estudio.
“Además, hemos realizado un análisis de secuenciación masiva de ARN con distintas variantes mutantes de RcsB en residuos catalíticos que modulan su fosforilación. Así, se han observado cambios en los niveles de expresión de cientos de genes, algunos relacionados con el metabolismo del hierro y desconocidos con anterioridad como controlados por RscB”, apunta Patricia Cansino, investigadora de la Universitat de València y coautora del estudio.
Para el investigador del CNB-CSIC Francisco García-Portillo, coautor del trabajo "una de las sorpresas del trabajo ha sido encontrar potenciales sitio de unión a ADN de este regulador en regiones que codifican a proteína además de las clásicas regiones promotoras". "Será interesante conocer en un futuro si a unión a estos sitios intragénicos la realiza RcsB de forma autónoma o con otros co-reguladores como ocurre en algunas regiones promotoras por las que muestra afinidad"
Finalmente, se cruzaron los datos obtenidos mediante el análisis de RNAseq y el mapeo genómico validando la unión de RcsB a dichas regiones. Los nuevos hallazgos han sido obtenidos mediante aproximaciones estructurales y funcionales combinadas con transcriptómica y bioinformática. El estudio ha permitido arrojar luz sobre cómo RcsB podría controlar la expresión de un número tan elevado de genes en respuesta a daños en la envuelta, y desvelar nuevos genes regulados por esta potencial diana de antimicrobianos.
Referencia:
Huesa J, Giner-Lamia J, Pucciarelli MG, Paredes-Martíınez F, García-del Portillo F, Marina A and Casino P. Structure-based analyses of Salmonella RcsB variants unravel new features of the Rcs regulon, Nucleic Acids Research 2021,DOI: 10.1093/nar/gkab060
Casa de la Ciencia. Delegación del CSIC en la Comunidad Valenciana